Projet Trophique
Contexte :
Dans le domaine de la biologie, les réseaux jouent un rôle essentiel dans la représentation des interactions, par exemple des interactions trophiques. Une chaîne trophique décrit le transfert d'énergie entre différents niveaux trophiques des producteurs jusqu'aux consommateurs terminaux. Les réseaux trophiques, quant à eux, sont des représentations montrant comment les différentes espèces interagissent dans leurs relations trophiques. (Paugy et Lévêque, 2006).
Une caractéristique importante des réseaux est leur organisation en groupes dans lesquels des nœuds partagent des caractéristiques similaires. Dans le contexte des réseaux trophiques, les nœuds correspondent à des espèces et les liens représentent des interactions (présentes ou absentes).
La détection de communauté est une technique d'analyse des réseaux trophiques. Elle permet de simplifier et de comprendre leurs structures complexes en identifiant les groupes fonctionnels d'espèces connectées entre elles et en mettant en avant les interactions clés au sein de ces réseaux. Les interactions peuvent être de différents types comme de la compétition ou de la facilitation entre les espèces d’un écosystème.
Les groupes fonctionnels peuvent prendre la forme de modules ou de guildes. Les guildes sont déterminées par une densité de partition externe maximale, regroupant des nœuds fortement connectés avec des nœuds externes, par opposition aux liens internes. Les modules sont ceux trouvés au maximum de la densité de partition interne. Les modules, quant à eux, sont identifiés par une densité de partition interne maximale, regroupant des nœuds fortement connectés entre eux à l'intérieur du groupe, par opposition aux liens externes. (Pascual-García et Bell, 2019).
Le but du Projet Trophique est de répondre à plusieurs problématiques. Tout d’abord, comment les groupes se structurent-ils quand ils interagissent? Est-il possible d’extraire les guildes d’un réseau trophique à l’aide d’une ou plusieurs méthodes de détection préexistantes? Enfin, comment évaluer la qualité de la représentation? Il s’agira de vérifier si les espèces se regroupent en guildes au vue des données disponibles. Dix-sept réseaux trophiques ont été mis à disposition.
Il serait également pertinent d’étudier l'influence de la disparition d’une ou de plusieurs espèces au sein du réseau. Cela pourrait permettre d’étudier la robustesse et la résilience des communautés. La robustesse d’un écosystème ou d’une espèce est la capacité à maintenir les fonctions face à des perturbations. La résilience est la capacité à récupérer un fonctionnement antérieur après avoir subi une perturbation.
Partie prenantes du projets :
Le produit :
Le produit fini se décline en quatre scripts : Importation, Clustering, Caractéristique et Représentation.
Le script “Importation” permet d’importer un jeu de données sous la forme d’un dataframe ou d’une matrice d’adjacence. Les dataset qui ont été utilisés sont ceux de la publication Kéfi et al. (2016), de la publication Allesina et Pascual (2009) et les datasets Donana, Norwood et Tatoosh de la publication Sander, Wootton et Allesina (2015).
Ce script permet d’obtenir un graphe ; un objet de type igraph qui est utilisé par la suite pour réaliser le clustering.
Le script “Clustering” permet d’utiliser l’algorithme pour détecter les guildes dans le réseau.
Le script “Caractéristique” permet d’extraire les informations des sous-groupes (nombre de guildes, nombre d'espèces dans chaque guilde, liste de chaque guilde avec le détail des noms des espèces). Il permet aussi d’obtenir des informations sur le réseau en lui-même (les liens entre chaque guilde, leur poids au sein du réseau).
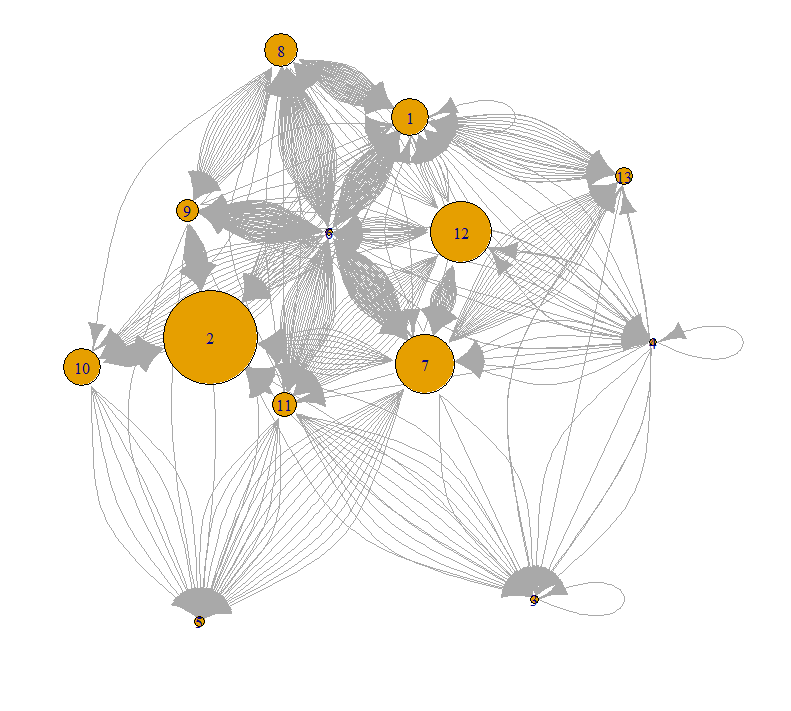
Le script “Représentation” permet d’obtenir des représentations macro (uniquement les groupes, voir figures 1 et 2) et micro (les espèces et leurs groupes, voir figure 3) des guildes dans le réseau.
Figure 1 : Représentation graphique du réseau macro : la taille du noeud est dépendante du nombre de liens total
Figure 2 : Représentation graphique du réseau macro : ne sont représentés que les liens entre les guildes
Figure 3 : Représentation graphique du réseau micro (les espèces en orange) avec le réseau macro (les plages de couleur)